Charakterisierung des Toponoms von Gewebe und Zellen mit Hilfe der MELC (Multi-Epitope-Ligand-Cartography)-Technik
Der Toponom-Arbeitskreis unter der Leitung von Dr. Ostalecki beschäftigt sich mit der Charakterisierung von Zellkulturen und Gewebe mit Hilfe der innova-tiven MELC- Technologie. MELC steht für Multi Epitope Ligand Cartography.
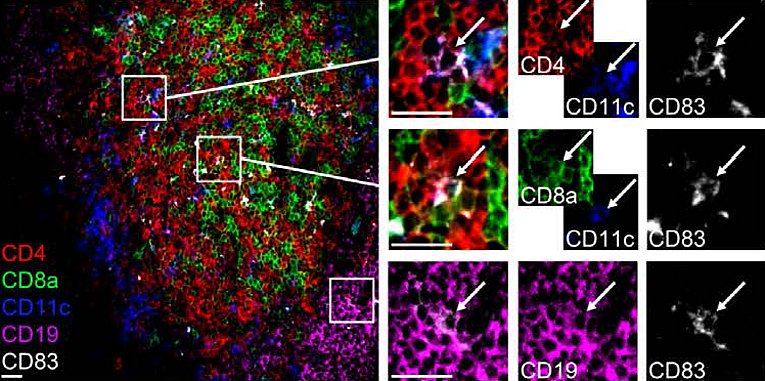
Diese Technik erlaubt es, 100 Antigene auf ein und demselben Gewebeschnitt anzufärben (Nat Biotech 2006) und die toponomische Anordnung qualitativ und semi-quantitativ zu erfassen.
Diese Methode wurde nun angewandt, um eine großes Panel von murinen Leukozyten-Subpopulationen an einem einzigen Gewebeschnitt eines peripheren Lymphknotens zu identifizieren. Die daraus resultierende Antikörper-Bibliothek wurde eingesetzt, um gesundes und entzündetes Gewebe vom Gehirn und Rückenmark im EAE (experimental autoimmune encephalomyelitis) Model zu charakterisieren. Die Anwesenheit und Aktivität der spezifischen Leukozyten- Subpopulationen (verschiedene T-Zellen, Dendritische Zellen, Makrophagen usw.) wurden untersucht und die Ergebnisse mit quantitativer RT-PCR korreliert (Eckert et al., 2013).
Ein weiterer Schwerpunkt unserer Forschung war die Erweiterung der Anwendung der MELC-Technik von Cryo-Schnitten auf Formalin-fixierte, in Paraffine eingebettete (FFPE) Gewebeschnitte. Dadurch wurde es möglich, die MELC-Technik mit ihrer immunhistochemischen Färbung mit einer automatischen auf magnetischen bead-basierenden RNA-Extraktionsmethode und anschließender RT-qPCR-Analyse zu kombinieren und beide Informationen aus aufeinanderfolgenden Schnitten zu bekommen. Dadurch kann RNA- und Protein-Information direkt zusammengebracht werden und neue Ansatzpunkte für indivualisierte Medizin bieten (Ostalecki et al. 2013).
Ferner wurde ein Projekt in der Melanom-Forschung durchgeführt. Dabei wurde die toponomischen Veränderungen im Gewebe und in Zellkulturen bei der Behandlung mit dem Medikament Sorafenib, einem Kinase-Hemmer charakterisiert. Und es wurde eine Industriekooperation mit Beiersdorf aufgebaut, bei der es um den Einsatz der MELC-Technik für die Forschung auf dem Gebiet der Hautalterung ging.
Die MELC-Technik besitzt ein sehr großes Potential, in verschiedenen Forschungsschwerpunkten und Kooperationen mit anderen Gruppen eingesetzt zu werden und so gezielte Fragestellungen in Grundlagenforschung, angewandter Medizin und Diagnostik zu beantworten.
Publikationen
Ostalecki C, Lee JH, Dindorf J, Collenburg L, Schierer S, Simon B, Schliep S, Kremmer E, Schuler G, Baur AS. Multiepitope tissue analysis reveals SPPL3-mediated ADAM10 activation as a key step in the transformation of melanocytes. Sci Signal. 2017, 10, eaai8288
Ostalecki C, Wittki S, Lee JH, Geist MM, Tibroni N, Harrer T, Schuler G, Fackler OT, Baur AS. HIV Nef- and Notch1-dependent Endocytosis of ADAM17 Induces Vesicular TNF Secretion in Chronic HIV Infection. EBioMedicine. 2016, 13, 294-304
Ostalecki C, Konrad A, Thurau E, Schuler G, Croner RS, Pommer AJ, Stürzl M. Combined multi-gene analysis at the RNA and protein levels in single FFPE tissue sections. Exp Mol Pathol. 2013, 95, 1-6
Eckhardt J, Ostalecki C, Kuczera K, Schuler G, Pommer AJ, Lechmann M. Murine whole-organ immune cell populations revealed by multi-epitope-ligand cartography. J Histochem Cytochem. 2013 , 61, 125-33